النبات

مواضيع عامة في علم النبات

الجذور - السيقان - الأوراق

النباتات الوعائية واللاوعائية

البذور (مغطاة البذور - عاريات البذور)

الطحالب

النباتات الطبية


الحيوان

مواضيع عامة في علم الحيوان

علم التشريح

التنوع الإحيائي

البايلوجيا الخلوية


الأحياء المجهرية

البكتيريا

الفطريات

الطفيليات

الفايروسات


علم الأمراض

الاورام

الامراض الوراثية

الامراض المناعية

الامراض المدارية

اضطرابات الدورة الدموية

مواضيع عامة في علم الامراض

الحشرات


التقانة الإحيائية

مواضيع عامة في التقانة الإحيائية


التقنية الحيوية المكروبية

التقنية الحيوية والميكروبات

الفعاليات الحيوية

وراثة الاحياء المجهرية

تصنيف الاحياء المجهرية

الاحياء المجهرية في الطبيعة

أيض الاجهاد

التقنية الحيوية والبيئة

التقنية الحيوية والطب

التقنية الحيوية والزراعة

التقنية الحيوية والصناعة

التقنية الحيوية والطاقة

البحار والطحالب الصغيرة

عزل البروتين

هندسة الجينات


التقنية الحياتية النانوية

مفاهيم التقنية الحيوية النانوية

التراكيب النانوية والمجاهر المستخدمة في رؤيتها

تصنيع وتخليق المواد النانوية

تطبيقات التقنية النانوية والحيوية النانوية

الرقائق والمتحسسات الحيوية

المصفوفات المجهرية وحاسوب الدنا

اللقاحات

البيئة والتلوث


علم الأجنة

اعضاء التكاثر وتشكل الاعراس

الاخصاب

التشطر

العصيبة وتشكل الجسيدات

تشكل اللواحق الجنينية

تكون المعيدة وظهور الطبقات الجنينية

مقدمة لعلم الاجنة


الأحياء الجزيئي

مواضيع عامة في الاحياء الجزيئي


علم وظائف الأعضاء


الغدد

مواضيع عامة في الغدد

الغدد الصم و هرموناتها

الجسم تحت السريري

الغدة النخامية

الغدة الكظرية

الغدة التناسلية

الغدة الدرقية والجار الدرقية

الغدة البنكرياسية

الغدة الصنوبرية

مواضيع عامة في علم وظائف الاعضاء

الخلية الحيوانية

الجهاز العصبي

أعضاء الحس

الجهاز العضلي

السوائل الجسمية

الجهاز الدوري والليمف

الجهاز التنفسي

الجهاز الهضمي

الجهاز البولي


المضادات الميكروبية

مواضيع عامة في المضادات الميكروبية

مضادات البكتيريا

مضادات الفطريات

مضادات الطفيليات

مضادات الفايروسات

علم الخلية

الوراثة

الأحياء العامة

المناعة

التحليلات المرضية

الكيمياء الحيوية

مواضيع متنوعة أخرى

الانزيمات
Excision Repair Systems in E. coli
المؤلف:
JOCELYN E. KREBS, ELLIOTT S. GOLDSTEIN and STEPHEN T. KILPATRICK
المصدر:
LEWIN’S GENES XII
الجزء والصفحة:
19-4-2021
2364
Excision Repair Systems in E. coli
KEY CONCEPTS
- The uvr system makes incisions 12 bases apart on both sides of damaged DNA, removes the DNA between them, and resynthesizes new DNA.
- Transcribed genes are preferentially repaired when DNA damage occurs.
Excision repair systems vary in their specificity, but share the same general features. Each system removes mispaired or damaged bases from DNA and then synthesizes a new stretch of DNA to replace them. A general pathway for excision repair is illustrated in FIGURE 1.

FIGURE 1. Excision repair removes and replaces a stretch of DNA that includes the damaged base(s).
In the incision step, the damaged structure is recognized by an endonuclease that cleaves the DNA strand on both sides of the damage.
In the excision step, a 5′→3′ exonuclease removes a stretch of the damaged strand. Alternatively, a helicase can displace the damaged strand, which is subsequently degraded.
In the synthesis step, the resulting single-stranded region serves as a template for a DNA polymerase to synthesize a replacement for the excised sequence. Synthesis of the new strand can be associated with removal of the old strand, in one coordinated action. Finally, DNA ligase covalently links the 3′ end of the new DNA strand to the original DNA.
The E. coli uvr system of excision repair includes three genes (uvrA, uvrB, and uvrC), which encode the components of a repair endonuclease. These proteins function in the stages indicated in FIGURE 2. First, a UvrAB dimer recognizes pyrimidine dimers and other bulky lesions. Next, UvrA dissociates (this requires adenosine triphosphate [ATP]), and UvrC joins UvrB. The UvrBC complex makes an incision on each side: one that is seven nucleotides from the 5′ side of the damaged site and another that is three to four nucleotides away from the 3′ side. This also requires ATP. UvrD is a helicase that helps to unwind the DNA to allow release of the single strand between the two cuts. The enzyme that excises the damaged strand is DNA polymerase I. The enzyme involved in the repair synthesis also is likely to be DNA polymerase I (although DNA polymerases II and III can substitute for it).
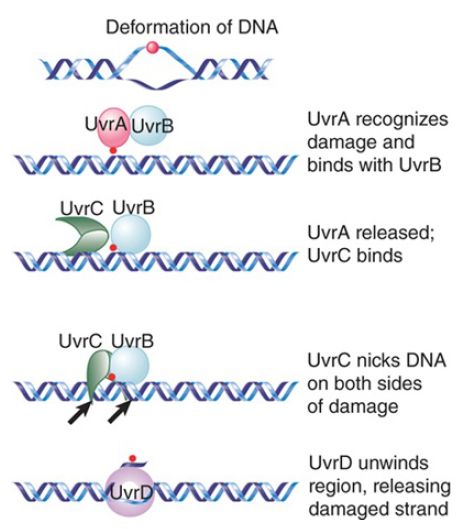
FIGURE 2. The Uvr system operates in stages in which UvrAB recognizes damage, UvrBC nicks the DNA, and UvrD unwinds the marked region.
UvrABC repair accounts for virtually all of the excision repair events in E. coli. In almost all cases (99%), the average length of replaced DNA is 12 nucleotides. (For this reason, the process is sometimes described as short-patch repair.) The remaining 1% of cases involves the replacement of stretches of DNA usually around 1,500 nucleotides long, but extending as much as 9,000 nucleotides (sometimes called long-patch repair). We do not know why some events trigger the long-patch rather than the short-patch mode.
The Uvr complex can also be directed to sites of damage by other proteins. Damage to DNA can result in stalled transcription, in which case a protein called Mfd displaces the RNA polymerase and recruits the Uvr complex. FIGURE 14.11 shows a model for the link between transcription and repair. When RNA polymerase encounters DNA damage in the template strand, it stalls because it cannot use the damaged sequences as a template to direct complementary base pairing. This explains the specificity of the effect for the template strand (damage in the nontemplate strand does not impede progress of the RNA polymerase).
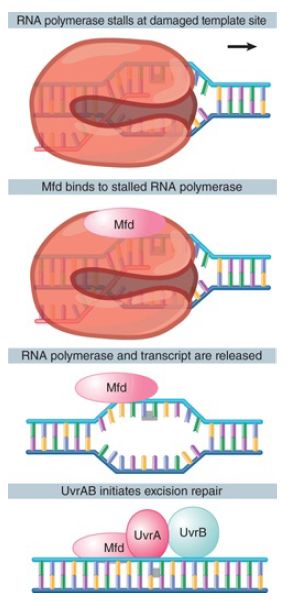
FIGURE 3. Mfd recognizes a stalled RNA polymerase and directs DNA repair to the damaged template strand.
The Mfd protein has two roles. First, it displaces the ternary complex of RNA polymerase from DNA. Second, it causes the UvrABC enzyme to bind to the damaged DNA, directing excision repair to the damaged strand. After the DNA has been repaired, the next RNA polymerase to traverse the gene is able to produce a normal transcript.
 الاكثر قراءة في مواضيع عامة في الاحياء الجزيئي
الاكثر قراءة في مواضيع عامة في الاحياء الجزيئي
 اخر الاخبار
اخر الاخبار
اخبار العتبة العباسية المقدسة

الآخبار الصحية















 قسم الشؤون الفكرية يصدر كتاباً يوثق تاريخ السدانة في العتبة العباسية المقدسة
قسم الشؤون الفكرية يصدر كتاباً يوثق تاريخ السدانة في العتبة العباسية المقدسة "المهمة".. إصدار قصصي يوثّق القصص الفائزة في مسابقة فتوى الدفاع المقدسة للقصة القصيرة
"المهمة".. إصدار قصصي يوثّق القصص الفائزة في مسابقة فتوى الدفاع المقدسة للقصة القصيرة (نوافذ).. إصدار أدبي يوثق القصص الفائزة في مسابقة الإمام العسكري (عليه السلام)
(نوافذ).. إصدار أدبي يوثق القصص الفائزة في مسابقة الإمام العسكري (عليه السلام)