النبات

مواضيع عامة في علم النبات

الجذور - السيقان - الأوراق

النباتات الوعائية واللاوعائية

البذور (مغطاة البذور - عاريات البذور)

الطحالب

النباتات الطبية


الحيوان

مواضيع عامة في علم الحيوان

علم التشريح

التنوع الإحيائي

البايلوجيا الخلوية


الأحياء المجهرية

البكتيريا

الفطريات

الطفيليات

الفايروسات


علم الأمراض

الاورام

الامراض الوراثية

الامراض المناعية

الامراض المدارية

اضطرابات الدورة الدموية

مواضيع عامة في علم الامراض

الحشرات


التقانة الإحيائية

مواضيع عامة في التقانة الإحيائية


التقنية الحيوية المكروبية

التقنية الحيوية والميكروبات

الفعاليات الحيوية

وراثة الاحياء المجهرية

تصنيف الاحياء المجهرية

الاحياء المجهرية في الطبيعة

أيض الاجهاد

التقنية الحيوية والبيئة

التقنية الحيوية والطب

التقنية الحيوية والزراعة

التقنية الحيوية والصناعة

التقنية الحيوية والطاقة

البحار والطحالب الصغيرة

عزل البروتين

هندسة الجينات


التقنية الحياتية النانوية

مفاهيم التقنية الحيوية النانوية

التراكيب النانوية والمجاهر المستخدمة في رؤيتها

تصنيع وتخليق المواد النانوية

تطبيقات التقنية النانوية والحيوية النانوية

الرقائق والمتحسسات الحيوية

المصفوفات المجهرية وحاسوب الدنا

اللقاحات

البيئة والتلوث


علم الأجنة

اعضاء التكاثر وتشكل الاعراس

الاخصاب

التشطر

العصيبة وتشكل الجسيدات

تشكل اللواحق الجنينية

تكون المعيدة وظهور الطبقات الجنينية

مقدمة لعلم الاجنة


الأحياء الجزيئي

مواضيع عامة في الاحياء الجزيئي


علم وظائف الأعضاء


الغدد

مواضيع عامة في الغدد

الغدد الصم و هرموناتها

الجسم تحت السريري

الغدة النخامية

الغدة الكظرية

الغدة التناسلية

الغدة الدرقية والجار الدرقية

الغدة البنكرياسية

الغدة الصنوبرية

مواضيع عامة في علم وظائف الاعضاء

الخلية الحيوانية

الجهاز العصبي

أعضاء الحس

الجهاز العضلي

السوائل الجسمية

الجهاز الدوري والليمف

الجهاز التنفسي

الجهاز الهضمي

الجهاز البولي


المضادات الميكروبية

مواضيع عامة في المضادات الميكروبية

مضادات البكتيريا

مضادات الفطريات

مضادات الطفيليات

مضادات الفايروسات

علم الخلية

الوراثة

الأحياء العامة

المناعة

التحليلات المرضية

الكيمياء الحيوية

مواضيع متنوعة أخرى

الانزيمات
Natural Resistance Genes
المؤلف:
John M Walker and Ralph Rapley
المصدر:
Molecular Biology and Biotechnology 5th Edition
الجزء والصفحة:
12-12-2020
2805
Natural Resistance Genes
The hypersensitive response often results from a specific interaction between a biotrophic pathogen and its host plant. This is known as a ‘gene-for-gene’ interaction between pathogen and host, in which an avirulence gene product from the pathogen is recognised by a resistance gene in the host plant. This recognition leads to induction of hypersensitive defence responses.
Avirulence (Avr) genes encode a variety of polypeptides, some of which may be required for pathogenicity but have then become avirulence factors once they have been detected by the plant. The best characterised Avr genes are Avr4 and Avr9 of the fungal pathogen Cladosporium fulvum. These encode pre-proteins which are processed to mature, extracellular cysteine-rich peptides of 86 and 28 amino acids, respectively. These peptides induce a hypersensitive response in plants which contain the matching resistance genes Cf-4 and Cf-9, respectively.
A series of plant resistance (R) genes active against a range of pathogens have been cloned and characterised. The R genes Cf-4 and Cf-9 encode transmembrane glycoproteins, in which the extracellular portion has characteristic leucine-rich repeats (LRR), a transmembrane domain and a C-terminal cytoplasmic domain. The Avr gene products are recognised by the LRR receptor regions, which results in signal transduction, gene activation and the hypersensitive response.
With the characterisation of R-genes against fungal, bacterial, viral and nematode pathogens, common patterns have emerged. Depending on the site of recognition of the elicitor, the R gene products may either span the plasma membrane and detect the elicitor extracellularly or be located in the cytoplasm for intracellular elicitor recognition. Intracellular recognition would be expected for virus infection, but pathogens growing extracellularly appear to be recognised by the presence of extracellular elicitors or signal molecules from the pathogens that cross the host plasma membrane.
Five classes of R-genes have been proposed (Table 1 and Figure 1), in which common features occur – leucine-rich repeats (LRR), nucleotide binding site (NBS), leucine zippers (LZ), toll and interleukin-
Table 1 Natural resistance genes characterised.
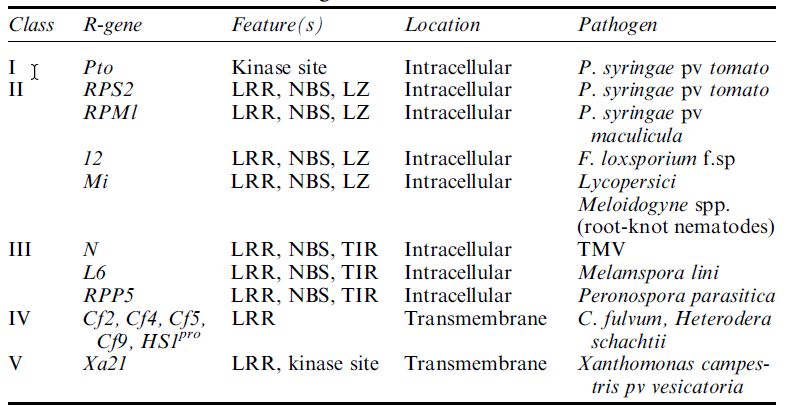
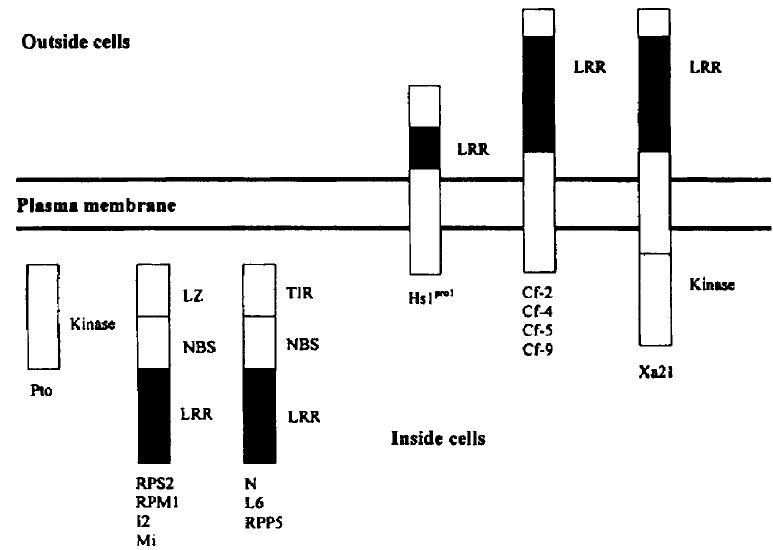
Figure 1 Diagnostic representation of different classes of resistance (R)-genes.
like receptors (TIR) and kinase sites.36 Some of these are shown in Table 10.3. Natural R-genes of this type can be transferred to other plants and, depending on the presence of elicitors/races of pathogen, may confer resistance in other plants. Modification of R-genes to alter the specificity of recognition of elicitors could also be achieved and various schemes have been developed to convert the specific recognition (e.g. of the avr9/ Cf9 system) to a general defence response switched on by damage caused by non-specific pathogens.
As indicated above, most of the R-genes identified so far have common sequence and structural motifs. It is possible to align published sequences and synthesize PCR primers complementary to the conserved sequences and to amplify classes of ‘resistance gene analogues’ (RGAs). RGAs can be mapped and exist in local clusters of related sequences in the genome. This approach can aid identification of natural resistance genes and mapping of RGAs can also provide molecular markers closely linked to known resistance genes.
However, not all R-genes operate via a gene-for-gene mechanism. The HM1 R-gene encodes a reductase which inactivates toxins produced by the fungal pathogen Cochliobulus carbonum and the mlo gene for powdery mildew resistance encodes a negative regulator of cell death.
 الاكثر قراءة في مواضيع عامة في الاحياء الجزيئي
الاكثر قراءة في مواضيع عامة في الاحياء الجزيئي
 اخر الاخبار
اخر الاخبار
اخبار العتبة العباسية المقدسة

الآخبار الصحية















 قسم الشؤون الفكرية يصدر كتاباً يوثق تاريخ السدانة في العتبة العباسية المقدسة
قسم الشؤون الفكرية يصدر كتاباً يوثق تاريخ السدانة في العتبة العباسية المقدسة "المهمة".. إصدار قصصي يوثّق القصص الفائزة في مسابقة فتوى الدفاع المقدسة للقصة القصيرة
"المهمة".. إصدار قصصي يوثّق القصص الفائزة في مسابقة فتوى الدفاع المقدسة للقصة القصيرة (نوافذ).. إصدار أدبي يوثق القصص الفائزة في مسابقة الإمام العسكري (عليه السلام)
(نوافذ).. إصدار أدبي يوثق القصص الفائزة في مسابقة الإمام العسكري (عليه السلام)